Utilisation de profils d'expression géniques pour la prédiction d'activité biologique de composés
Je travaille principalement au développement d’un modèle d’intelligence artificielle visant à prédire l’effet de composés chimiques sur des lignées cellulaires cancéreuses. L’objectif est d’identifier virtuellement des molécules susceptibles de constituer de bonnes candidates pour le développement de nouveaux médicaments. Dans ce cadre, je collabore étroitement avec le Pr Quentin Fournier, chercheur associé au Mila et professeur associé au DIRO, ainsi qu’avec son étudiante au doctorat, Lola Le Breton.
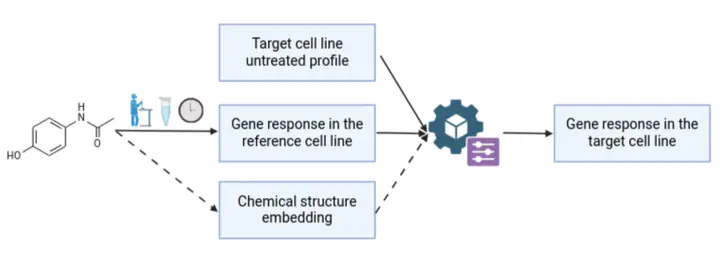
Nous définissons un « traitement » comme l’exposition d’une cellule (ou d’une lignée cellulaire) à une molécule donnée, à une dose et pendant une durée spécifiques. Notre hypothèse est que les changements d’expression génique induits par un traitement constituent une représentation informative de celui-ci. Nous appelons profile delta l’ensemble de ces changements, définis comme la différence entre le profil d’expression traité et le profil non traité.
Nous entraînons un modèle à prédire le profile delta d’une lignée cellulaire cible soumise à un traitement, à partir de deux éléments : (i) le profil d’expression non traité de cette lignée cible, et (ii) le profile delta observé dans une lignée cellulaire de référence exposée au même traitement, mais non apparentée à la lignée cible. Cette approche, fondée sur une représentation biologique directe du traitement, conduit à de meilleures performances que les méthodes reposant uniquement sur la structure chimique de la molécule. Nous explorons néanmoins l’apport potentiel d’embeddings de structures chimiques issus de modèles fondationnels, afin d’évaluer s’ils peuvent améliorer davantage les performances du modèle.